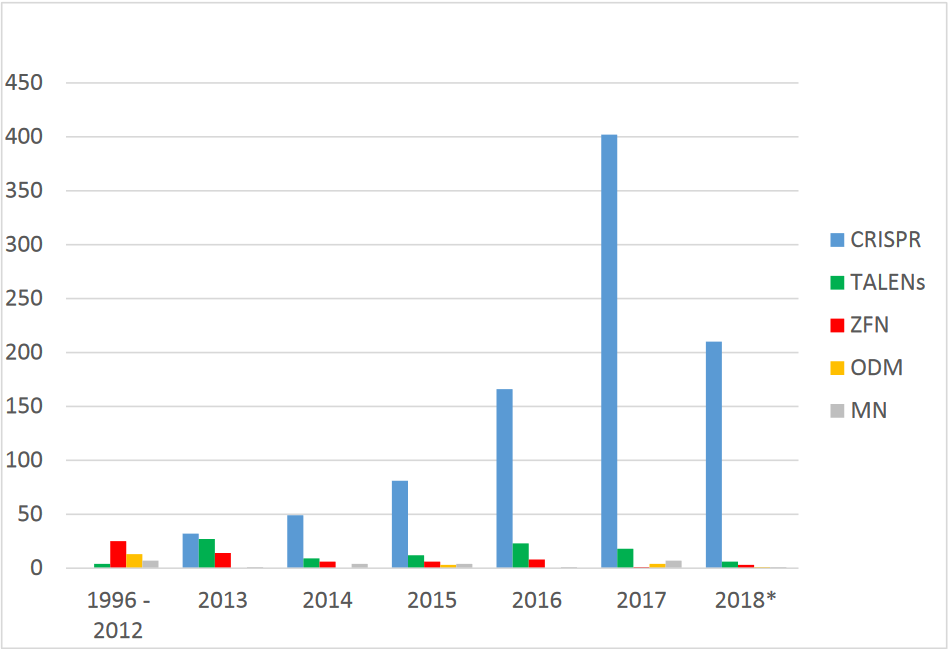
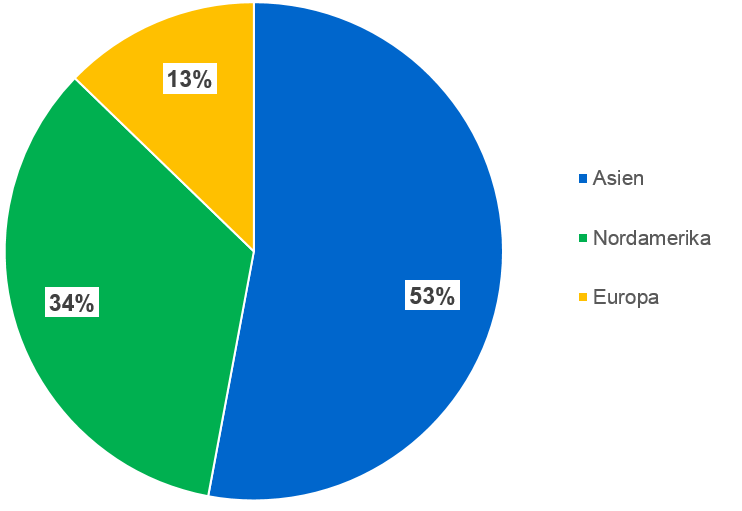
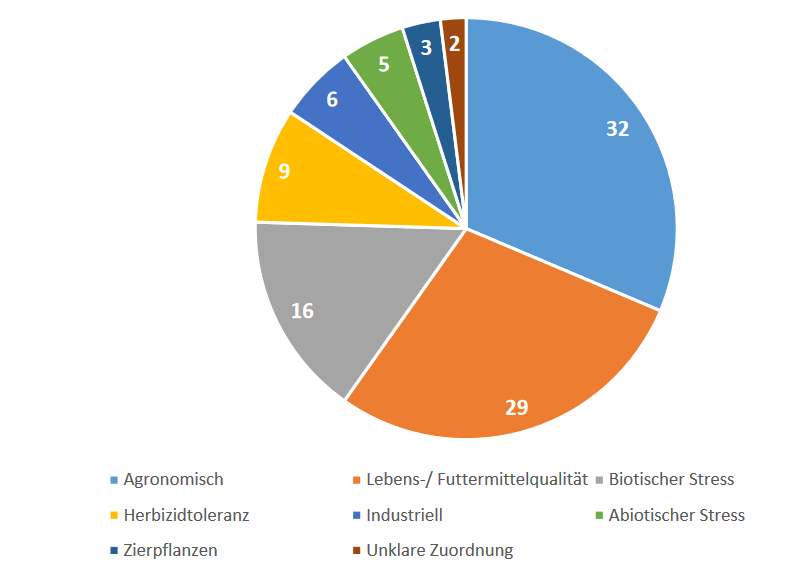
Im Folgenden möchte ich nun an vier konkreten Anwendungsbeispielen aufzeigen, was mit Genome Editing bereits jetzt möglich ist und welche Vorteile diese Art der Züchtung gegenüber etablierten Züchtungstechniken hat.
Anwendung 1: Reduzierter Arsengehalt in Reis
Arsen ist ein chemisches Element, welches natürlicherweise in der Erdkruste vorhanden ist und über das Grundwasser in unsere Nahrung gelangt. Da Reis meist auf überfluteten Feldern angebaut wird, ist er besonders anfällig für eine Arsenanreicherung in der Pflanze und den Körnern. Arsenrückstände verursachen bei übermäßiger Einnahme gesundheitliche Probleme wie Hautveränderungen, Gefäß- und Nervenschädigungen, bis hin zu Krebserkrankungen. Dies ist der Grund dafür, dass es für anorganisches Arsen in der EU-Grenzwerte von 0,2 bis 0,3 mg/kg gibt. In Lebensmitteln für Säuglinge dürfen sogar nur 0,1 mg/kg anorganisches Arsen enthalten sein. Neben veränderten Anbaubedingungen, die jedoch mit einem Ertragsverlust einhergehen, spielt die Sortenwahl eine entscheidende Rolle bei der Arsenreduzierung. Deshalb rät die WHO Reissorten zu züchten, die weniger Arsen aufnehmen [18]. Chinesische Wissenschaftler der Sun Yat-sen Universität haben ein Gen identifiziert, welches für den Arsentransport in die Pflanze verantwortlich ist. Dieses Gen wurde mit der CRISPR/Cas Technik ausgeschaltet, wodurch der Transport von Arsen in die Pflanze und die Einlagerung im Reiskorn verringert wurden [19, 20]. Die Ergebnisse liefern wichtige Erkenntnisse, um Sorten mit verminderten Arsenrückständen zu züchten.
Es gibt bereits heute konventionell gezüchtete Sorten, die eine erhöhte Arsentoleranz aufweisen. Hat man jedoch eine Reissorte A mit guten Ertrags- und Qualitätseigenschaften, die aber keine Arsentoleranz besitzt, hat man zwei Möglichkeiten: 1. Man benutzt Genome Editing in Reissorte A, um – wie oben beschrieben – direkt die Arsentoleranz in der Pflanze zu bekommen oder 2. Man kreuzt die Reissorte A mit einer arsentoleranten Sorte B. Das Problem bei letzterem Vorgehen ist jedoch, dass neben der gewünschten Eigenschaft (nach den Regeln der Vererbungslehre) die Tochtergeneration (also das Produkt der Kreuzung) jeweils die Hälfte der Gene von Sorte A und Sorte B in sich trägt. Um alle ungewünschten Eigenschaften der Wildsorte wieder loszuwerden, kann man Pflanzen „rückkreuzen“. Das bedeutet, dass man die Tochtergeneration wieder mit der Ausgangssorte A kreuzt. Diesen Schritt der Rückkreuzung führt man mehrere Male, jeweils mit der Ausgangssorte A, durch und selektiert stets auf die Eigenschaft der Arsentoleranz. Nach circa sieben Generationen erhält man eine Reissorte, die (fast) alle Eigenschaften der Reissorte A besitzt und zusätzlich die Eigenschaft der Arsentoleranz. Wie anhand dieser Ausführung gut zu erkennen ist, benötigt diese Methode viele Jahre und ist mit viel Arbeits- und Selektionsaufwand (zur Identifizierung der arsentoleranten Pflanzen) verbunden. Mit Genome Editing kann man das gleiche Ergebnis in viel kürzerer Zeit erreichen, weil man das gewünschte Gen eben direkt einbaut und den Rest des Genoms unbehelligt lässt. Das Endprodukt unterscheidet sich unabhängig von der gewählten Methode kaum voneinander.
Anwendung 2: Veränderte Stärkezusammensetzung in Kartoffel
Neben dem Anbau von Kartoffeln als Nahrungsmittel, wird Kartoffelstärke auch industriell verwendet. Stärke (zählt zu den Kohlenhydraten) ist ein wesentlicher Bestandteil in Kartoffeln und besteht aus zwei Komponenten: Amylopektin (zu ca.75%) und Amylose (zu ca. 25%). Für die industrielle Stärkenutzung, z.B. für Kleb- und Schmierstoffe, wird lediglich Amylopektin benötigt. Deshalb müssen die beiden Stärketypen voneinander getrennt werden. Dies ist mit chemischen, physikalischen oder enzymatischen Verfahren zwar möglich, jedoch arbeitsintensiv und kann je nach Verfahren zu Umweltbelastungen führen. Wissenschaftlern der Swedish University of Agricultural Sciences ist es gelungen, mithilfe von CRISPR/Cas ein Gen auszuschalten, das für die Amylosebildung verantwortlich ist. Das Resultat ist eine Kartoffel, die ausschließlich Amylopektin bildet, wodurch der anschließende Trennungsaufwand entfällt [17].
Hier ist anzumerken, dass es bereits die konventionell gezüchtete Kartoffelsorte Eliane gibt, die durch ungerichtete Mutagenese (Strahlung) erzeugt wurde. Bei der ungerichteten Mutagenese wird Saatgut mit Chemikalien oder Strahlung behandelt, was unspezifische Mutationen an vielen Stellen im Genom auslöst (siehe Tabelle 1). Um daraus wieder vitale Pflanzen zu bekommen, sind auch hier aufwendige Rückkreuzungsarbeiten notwendig. Das Endprodukt ist unabhängig von der verwendeten Züchtungstechnik eine Kartoffel, die ausschließlich Amylopektin bildet.
Die folgende Tabelle stellt die wesentlichen Unterschiede zwischen Genome Editing und der ungerichteten Mutagenese dar:
Tabelle 1: Unterschiede zwischen Genome Editing und der ungerichteten Mutagenese in der Pflanzenzüchtung. Quelle: D. Modrzejewski
| |
Genome Editing |
Ungerichtete Mutagenese |
|
Anzahl der Mutationen
|
Eine |
sehr viele |
| Spezifität der Mutation(en) |
An spezifischer Stelle im Genom |
An (vielen) unspezifischen Stellen im Genom |
| Anzahl benötigter Pflanzen |
Wenige Pflanzen werden benötigt (aufgrund hoher Mutationsrate des Zielgens) |
Sehr viele Pflanzen werden benötigt (aufgrund sehr geringer Mutationsrate des Zielgens und schlechter Vitalität der Pflanze)
|
| Ungewollte Mutationen |
(meist) keine ungewollten Mutationen |
Viele ungewollte Mutationen an anderen Stellen im Genom |
| Rückkreuzung nötig |
Nein |
Ja |
| Benötigte Zeit |
Monate |
Viele Jahre |
Wie der Europäische Gerichtshof im vergangenen Jahr geurteilt hat, müssen alle Genom-editierten Pflanzen nach den Gentechnikregelungen zugelassen werden, was sehr zeitaufwendig und mit enormen Kosten verbunden ist. Werden Sorten dagegen mithilfe der ungerichteten Mutagenese gezüchtet, sind keine besonderen Sicherheitsprüfungen notwendig und die entsprechenden Sorten müssen lediglich den normalen Sortenzulassungsprozess durchlaufen.
Anwendung 3: Toleranz gegen die Grauschimmelfäule in Wein
Grauschimmel („Botrytis cinerea“) ist ein weit verbreiteter Schimmelpilz, der als Schädling über 2035 Wirtspflanzen befällt. Im Weinbau kann es bei feuchter Witterung oder bei Verletzung der Beeren beispielsweise infolge von Hagel, starken Niederschlägen oder Sonnenbrand (ja, auch Pflanzen können einen Sonnenbrand bekommen!) zu Problemen mit Botrytis cinerea kommen. Befällt der Pilz die unreifen Beeren, verursacht er Ertrags- und Qualitätseinbußen. Vor allem weichschalige Sorten wie Müller-Thurgau und Riesling sind anfällig. Kommt es trotz vorbeugenden Kulturmaßnahmen wie ausreichender Belüftung zum Befall, können als letztes Mittel Fungizide wie Teldor im konventionellen Anbau (bis zu zwei Anwendungen im Jahr) oder Kaliumhydrogencarbonat im Ökolandbau (bis zu sechs Anwendungen im Jahr) eingesetzt werden [21, 22].
Wissenschaftlern der Northwest A&F University in China ist es gelungen, mithilfe der CRISPR/Cas Technik gezielt eine Punktmutation in einem Gen zu erzeugen, das für seine tragende Rolle bei der biotischen Stressabwehr bekannt ist. Die Ergebnisse des Versuchs lieferten eine erhöhte Toleranz gegen den Grauschimmel [23]. Durch solche Ansätze kann der Einsatz von Pflanzenschutzmitteln reduziert werden und ein Beitrag für eine umweltschonendere Landwirtschaft geleistet werden.
Wie bereits im ersten Beispiel erwähnt, hat man auch hier die Möglichkeit das Resistenzgen aus einer Wildart einzukreuzen. Am Beispiel Reis dauern die benötigten sieben Rückkreuzungen sieben Jahre. Bei Wein, der erst im dritten Jahr blüht und erst dann rückgekreuzt werden kann, dauern sieben Rückkreuzung schon 21 Jahre. Erschwerendkommt hierbei hinzu, dass selbst nach sieben Rückkreuzungen noch „Reste“ der Wildart in der neu gezüchteten Sorte verbleiben, die den Geschmack der neu gezüchteten Sorte verfälschen können. Ein Unding für jeden Weingourmet…
Anwendung 4: Resistenz gegen CBSD Virus in Maniok [24]
Maniok ist ein wichtiges Grundnahrungsmittel in afrikanischen Ländern wie Burundi, Ruanda, Uganda, Kenia und Tansania und wird dort von vielen Kleinbauern angebaut. Es ist nach Mais, Reis, Weizen und Kartoffel die weltweit am häufigsten angebaute Nutzpflanze. Im Jahr 2011 hat die UN Food and Agriculture Organization (FAO) vor der Ausbreitung eines Pflanzenvirus gewarnt, das große Teile der Ernte und damit die Lebensgrundlage der Bevölkerung vernichtet. Das Virus ist verantwortlich für die Braunstreifenkrankheit (Cassava Brown Streak Disease (CBSD)) [25]. Es verfärbt die Maniokknolle bräunlich, wodurch sie ungenießbar wird. Das tückische daran ist, dass man den Pflanzenteilen, die über der Erde liegen, die Virusinfektion nicht ansieht und der Schaden erst nach der Ernte sichtbar wird.
In einem von der Bill & Melinda Gates Foundation unterstützen Arbeit, schafften es Forscher der University of California, durch das Ausschalten mehrerer Gene durch CRISPR/Cas, Maniokpflanzen zu erzeugen, die eine erhöhte Toleranz gegen die Braunstreifenkrankheit aufweisen.
Da das Thema Gentechnik in Entwicklungsländern sehr komplex ist, möchte ich an dieser Stelle Herr Professor Martin Qaim, Professor für Internationale Ernährungswirtschaft und Ländliche Entwicklung, von der Uni Göttingen zitieren: „Europäer können es sich leisten, gentechnisch veränderte Lebensmittel abzulehnen, Menschen auf anderen Kontinenten nicht. (…) Es geht gar nicht darum, dass die Gentechnik letztlich irgendwie der Schlüssel zur Lösung aller Probleme wäre, aber Gentechnik oder Genome Editing (…) bietet schon große Potenziale, tatsächlich Pflanzen hervorzubringen, die widerstandsfähiger sind, auch gegen zunehmenden Klimastress. (…) Was wir in Afrika jedoch sicherlich nicht brauchen, sind ganz, ganz starke Patente, also da warne ich vor. (…) Wir werden nicht umhinkommen, öffentliche Agrarforschung zu fördern, damit das, was im Kleinbauernsektor benötigt wird, auch tatsächlich entwickelt wird und dann auch von den Preisen her zugänglich für diese Bauern ist.“ [26]
Abschließend möchte ich noch meine persönliche Meinung darstellen:
Für eine progressive Agrarwende ist es essentiell hohe und stabile Erträge zu sichern und gleichzeitig die negativen Auswirkungen der Landwirtschaft auf die Umwelt und Artenvielfalt soweit wie möglich zu reduzieren. Dazu sollte man für jedes Problem überlegen, welche Methoden am besten geeignet sind, um diese zu lösen - anstatt einzelne Techniken von vornherein abzulehnen und lediglich mit den verbleibenden die Probleme anzugehen.